Samra Turajlic氏(The Francis Crick Institute)、Rong Fan氏(Yale University)、Christina Leslie氏(Memorial Sloan Kettering Cancer Center)らの学際的な専門家パネルにて、マルチオミクスを用いた研究の進歩と課題について解説します。
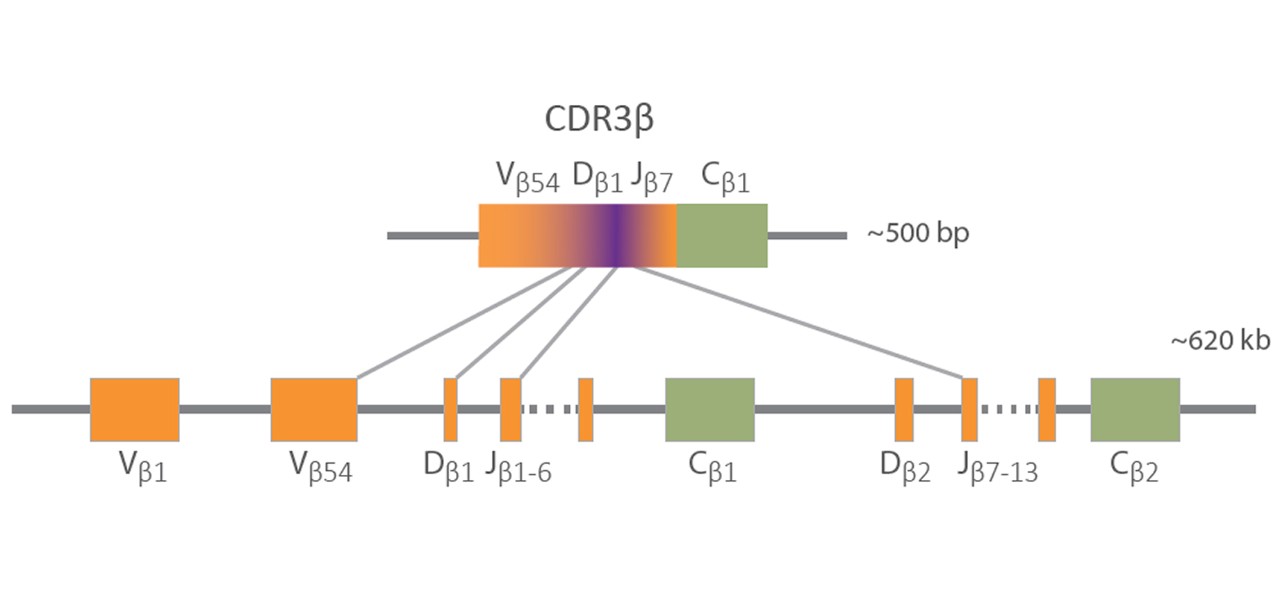
免疫レパトアシーケンス(IR-Seq)は、次世代シーケンサー(NGS)を使用して、B細胞受容体(BCR)とT細胞受容体(TCR)の多様性をプロファイリングします。1 IR-Seqにより、研究者はレパートリーの多様性とクローン性を特徴づけることができ、血液悪性腫瘍に関連する受容体配列を調べ、自己免疫疾患、IR-Seqは、BCRとTCRを高解像度で解析するために必要なスループットと感度を提供します。2健康と疾患における適応免疫に関する洞察を可能にします。
BCRおよびTCRシーケンスの免疫レパートリーは、感染症、自己免疫疾患、およびがんに応じて動的に変化します。循環抗原受容体のレパートリーは、多様なプールから、免疫反応中に拡大した抗原特異的クローンに支配されるプールへと変化します。したがって、免疫レパートリーの構成を理解することは、免疫介在性疾患の理解を深めるため、および治療開発に情報を与えるために不可欠です。3