ゲノムデータ圧縮
ロスレスゲノムデータ圧縮
Enancioのテクノロジで軽減されたゲノムデータの保存と転送コスト

ゲノムデータ圧縮のメリット
イルミナは革新的なシーケンステクノロジーを提供し、急増する次世代シーケンサー(NGS)データアウトプットを管理するお客様の手助けになるべく日夜取り組んでいます。Enancioのゲノムデータの可逆圧縮テクノロジーは、現在はORA(original read archive)として知られており(旧Lena)、最適レベルの処理速度と効率をもたらします。
ゲノムデータ圧縮のメリット:
- 低いデータ保存コスト
- 高速データファイル転送
- 内部ネットワークトラフィックの削減
ロスレスゲノムデータ圧縮テクノロジー
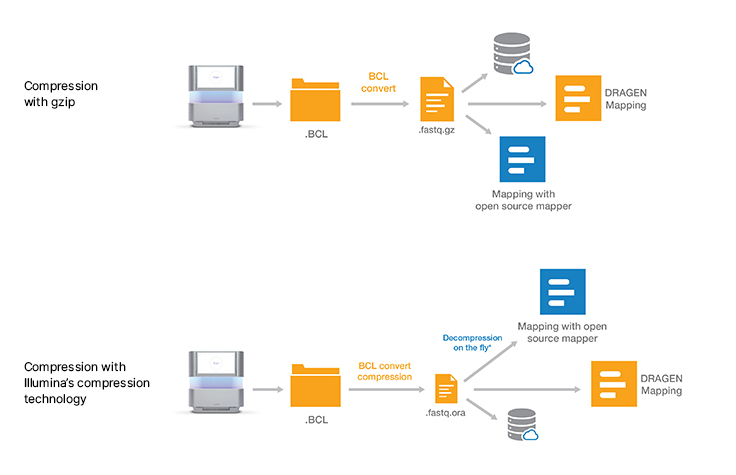
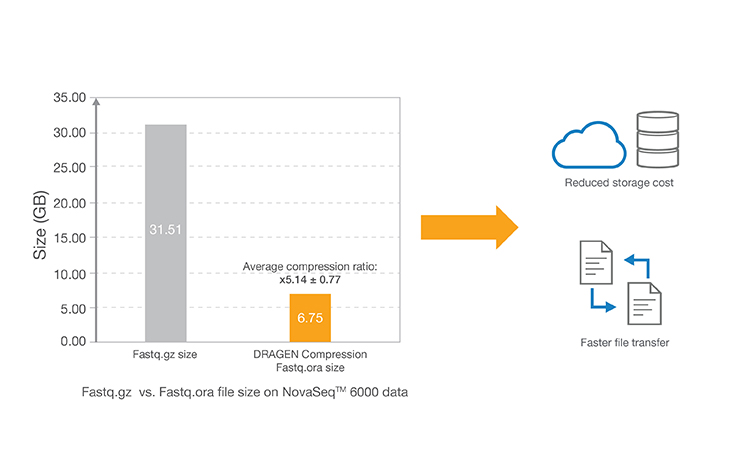
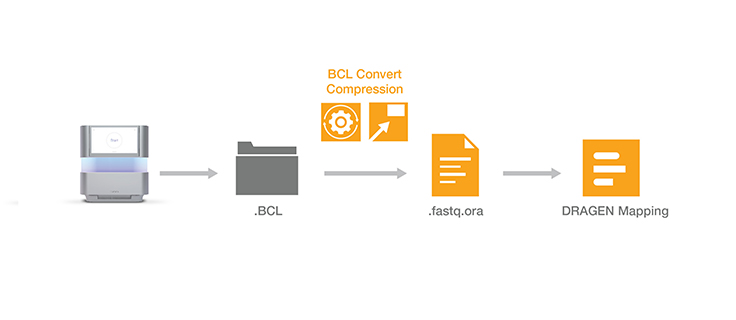
ロスレスゲノムデータ圧縮テクノロジーにより、イルミナシーケンスシステムからのアウトプットを圧縮する場合よりもデータストレージフットプリントを5倍削減することが可能です。ORA圧縮テクノロジーでは、リファレンスベースの圧縮方式を使用します。この方式では、超高速マッピングスキームで、読み取り値をリファレンスゲノムにマップし、それらの読み取り値の再現に必要なデータのみ(位置、差分リスト)を保存します。
Enancio以外のデータ圧縮テクノロジーでは、処理速度が低速になりがちです。ORAテクノロジーは、データの整合性を維持しながら、高圧縮率だけでなく高速圧縮と高速解凍にも最適化されています。クオリティスコアは、さまざまなクオリティスキームに採用されているレンジエンコーダーとコンテキストモデルを利用して、ロスレス方式でコード化されています。
DRAGEN ORA解凍ソフトウェアにアクセス
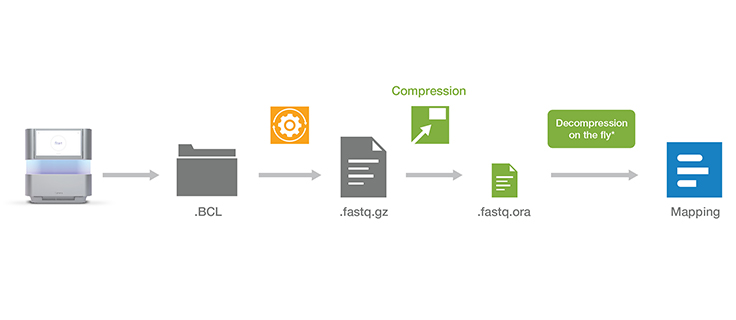
ORA圧縮テクノロジーで圧縮されたファイルはすべて弊社の解凍ソフトウェアで簡単に解凍できます。解凍ソフトウェアは無料でダウンロード、利用できます。
解凍ソフトウェアのダウンロード解凍ソフトウェアをいったんインストールすれば、BWA、STAR、Bowtieなど、さまざまな定評あるマッピングツールに、特別な準備をすることなく簡単なコマンドで、解凍ファイルのアウトプット先を直接パイプ処理できるようになります。圧縮/解凍テクノロジーもDRAGEN二次解析ソフトウェアに統合され、これによりシーケンスデータを正確に超高速解析することができます。

ロスレスゲノムの圧縮を装置内で実現
DRAGEN ORAロスレスゲノムデータ圧縮は、NextSeq 1000システム、NextSeq 2000システム、NovaSeq Xシリーズ、およびv3.8以降のDRAGEN二次解析サーバーで装置上で利用可能になりました。詳細はこちら:
圧縮テクノロジのFAQ
関連ソリューション
ゲノムデータの保存とセキュリティ
ビルトインの高速で拡張性を備えたクラウドで、大量のゲノム/NGSデータセットを安全に保存、処理、共有します。
シーケンシングデータ解析
弊社のシーケンスデータ解析ソフトウェアを使用すると、解析ワークフローの構成と実行にかかる時間が短縮されるため、研究に多くの時間をかけることができます。
イルミナインフォマティクス製品ポートフォリオ
ゲノムデータ解析と管理を合理化するためにデザインされたインフォマティクス製品のさまざまな品揃えをご紹介します。
圧縮テクノロジに関するご質問はありませんか?
詳しい内容については私どもにおたずねください。
参考文献
- NextSeq 1000およびNextSeq 2000システム、NovaSeq 6000システムで生成されたファイル上。
- この結果は、NovaSeq 6000システムで、有効範囲30xに設定してNA12878シーケンスを実施したDNAサンプルから得られました。データはBaseSpaceプロジェクトで公開しています:basespace.illumina.com/s/3ExEZMlH8Lkq。
- Li H. and Durbin R. Fast and accurate short read alignment with Burrows–Wheeler transform. Bioinformatics. 2009 Jul 15; 25(14): 1754–1760.
- Dobin A. et al. STAR: ultrafast universal RNA-seq aligner. Bioinformatics. 2013 Jan; 29(1): 15–21.
- Langmead B. et al. Ultrafast and memory-efficient alignment of short DNA sequences to the human genome. Genome Biology 2009 10:R25